Biotecnología de probióticos y patógenos intestinales
El intestino desempeña un papel fundamental en nuestro cuerpo, no solo en la absorción de nutrientes de los alimentos que ingerimos, sino también en albergar una compleja red de interacciones que involucran a los enterocitos intestinales (células que recubren el intestino), las bacterias del microbioma (microorganismos que habitan en el intestino) y el sistema inmunológico. Los cambios en estos factores pueden perturbar la estabilidad de estas interacciones, lo que permite que bacterias dañinas invadan el intestino y causen enfermedades.
En nuestro laboratorio de investigación, nos enfocamos en estudiar cómo las bacterias patógenas utilizan un mecanismo especializado llamado Sistema de Secreción Tipo 3 para infectar el intestino y evadir las defensas del sistema inmunológico. Estas bacterias emplean proteínas específicas conocidas como proteínas efectoras, que establecen una red de interacciones crucial para su proceso de infección. Nuestro objetivo es desentrañar esta red de interacciones de proteínas para comprender mejor cómo ocurren las infecciones y cómo responde el sistema inmunológico a diferentes estrategias de infección. Para lograr esto, hemos creado cepas mutantes de estas bacterias patógenas. Luego, utilizamos estos mutantes para infectar ratones y observar los efectos que tienen en el intestino. Esto nos permite obtener información sobre los mecanismos detrás de la infección y la inmunidad.
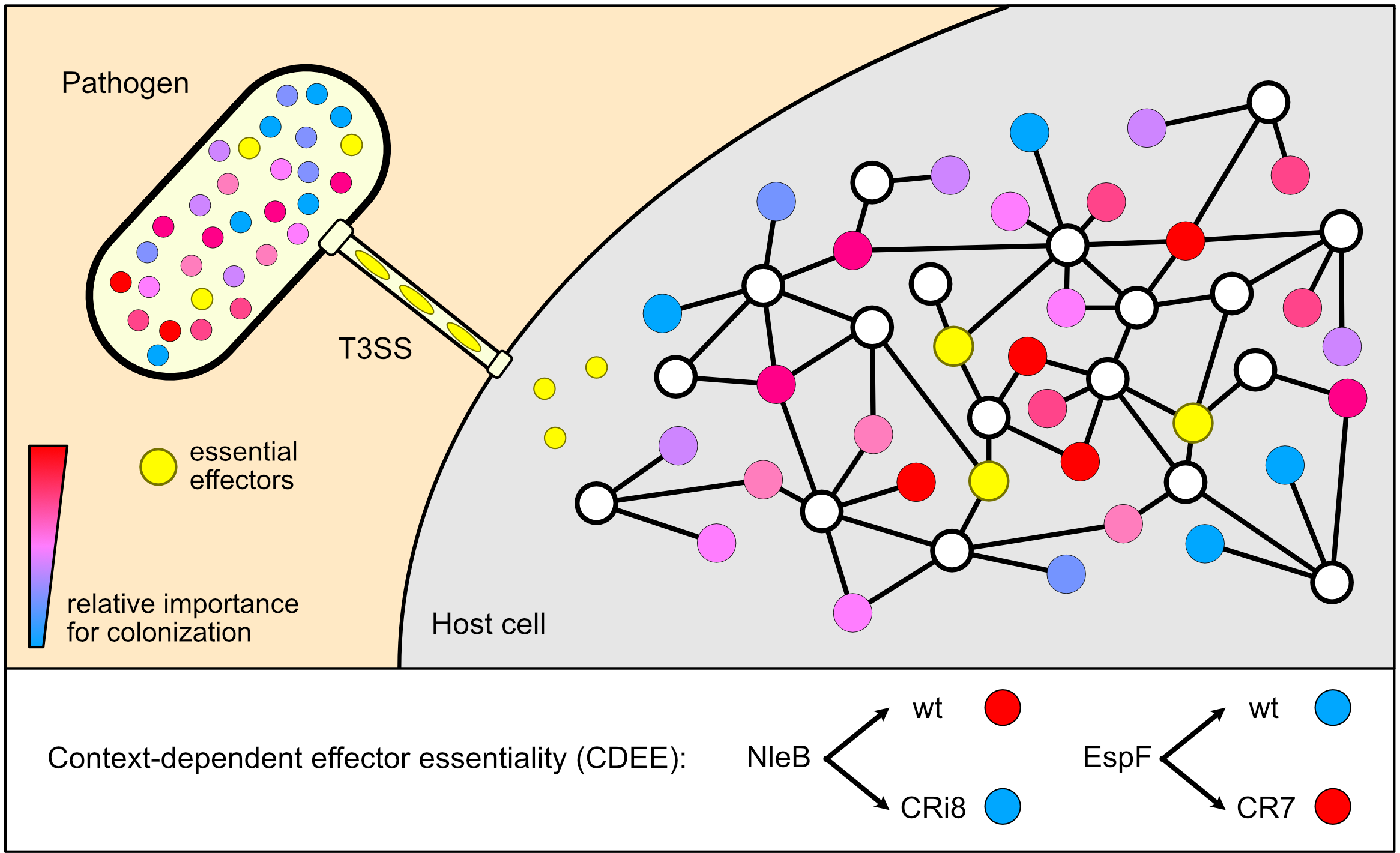
Figura 1. Los efectores del sistema de secreción tipo III (T3SS) forman redes interconectadas in vivo. Los patógenos inyectan proteínas efectoras de T3SS en las células huésped para interferir con los procesos celulares y así establecer la infección. Una vez infectados, estos efectores (representados como círculos de colores) pueden formar conexiones (líneas) con las proteínas del huésped (círculos blancos) y otros efectores, construyendo una red robusta que puede soportar perturbaciones significativas sin afectar la virulencia. Una proteína huésped puede estar conectada con más de un efector mediante bordes con naturaleza positiva/estimuladora y/o inhibidora negativa; por ejemplo, los efectores de T3SS NIeB y EspL de los patógenos de unión y barrido (A/E) pueden inhibir RIPK1 modificando su dominio de muerte o escindiendo su dominio RHIM respectivamente, mientras que los factores de intercambio de nucleótidos de guanina (GEF) de Salmonella, SopE y SopE2, pueden activar Rac1 y Cdc42, mientras que SptP, una proteína activadora de GTPasas (GAP), puede inactivar estas GTPasas. Aparte de los efectores que son esenciales en todas las redes (que se muestran en amarillo), la importancia de cada efector para la colonización in vivo depende de las conexiones que establece dentro de la subred; aquí, el color de cada efector indica su importancia relativa para la colonización. Este fenómeno se denomina esencialidad efectora dependiente del contexto (CDEE), ejemplificada aquí por NleB, que es necesaria para la colonización en la subred de tipo salvaje (WT) (en rojo) pero se vuelve prescindible en CRi8 (en azul), y EspF, que se vuelve necesario para la colonización en el contexto de la subred CR7 (en rojo).
Además, aspiramos a aprovechar el poder de los probióticos para aplicaciones biotecnológicas en el campo de la biomedicina. Utilizando técnicas avanzadas de biología sintética, pretendemos desarrollar métodos para manipular cepas de bacterias poco conocidas. Estas cepas bacterianas tienen el potencial de servir como indicadores de buena salud y ofrecer protección contra enfermedades intestinales. Nuestra investigación busca impulsar las capacidades de estos probióticos como herramientas valiosas para mejorar la salud humana.
| Apellidos | Nombre | Laboratorio | Ext.* | Categoría profesional | |
|---|---|---|---|---|---|
| Ruano Gallego | David | 104 | 4678 | druano[at]cbm.csic.es | Investigador |
| Bueno Alonso | Marina | 104 | 4678 | marina.buenoa@estudiante.uam.es | Estudiante TFG |




















